Paleontología Virtual
Día 7: Estimación de Mordida Máxima y Morfometría Geométrica
E. Miguel Díaz de León Muñoz
2026-04-27
Morfometría Geométrica (GMM)
Introducción a la Morfometría Geométrica (GMM)
Más allá de las medidas lineales
- Concepto clave: La morfometría geométrica es el estudio cuantitativo de la forma anatómica utilizando puntos topológicamente homólogos conocidos como landmarks (marcas anatómicas).
- Supera la limitación de usar simples medidas lineales (largo, ancho), conservando la geometría espacial completa de la estructura.
- Semi-landmarks: Para capturar la curvatura de estructuras o superficies fósiles que carecen de puntos homólogos discretos y claros, se emplean curvas y superficies formadas por puntos deslizantes (semi-landmarks).
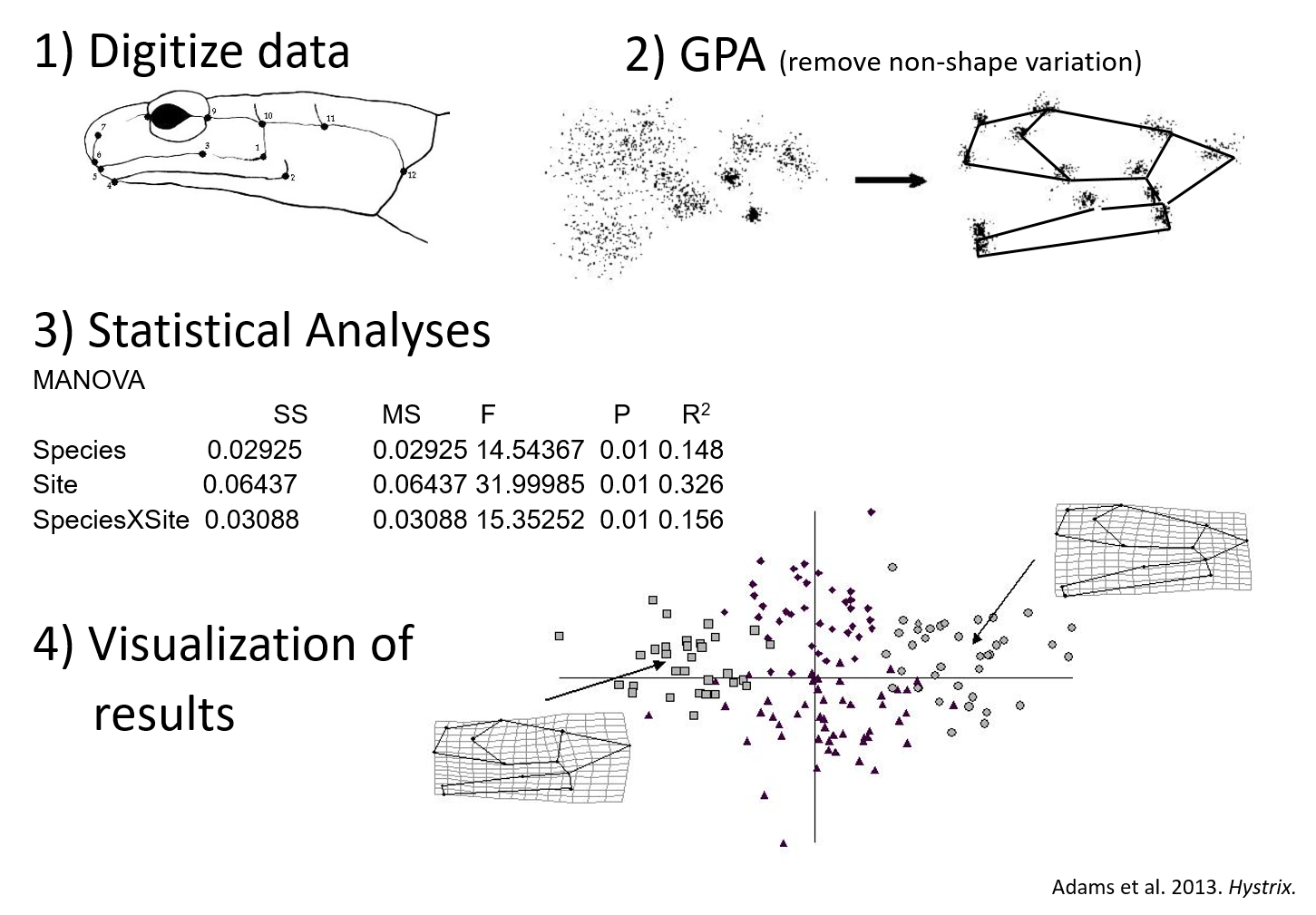
Superposición de Procrustes
Estandarización de la forma
- Antes de realizar análisis estadísticos, deben eliminarse las diferencias triviales de posición, escala y orientación.
- La superposición de Procrustes (GPA) remueve los efectos del tamaño absoluto, la rotación y la traslación de los modelos tridimensionales, permitiendo que solo las “formas” (shape) sean estrictamente comparables.
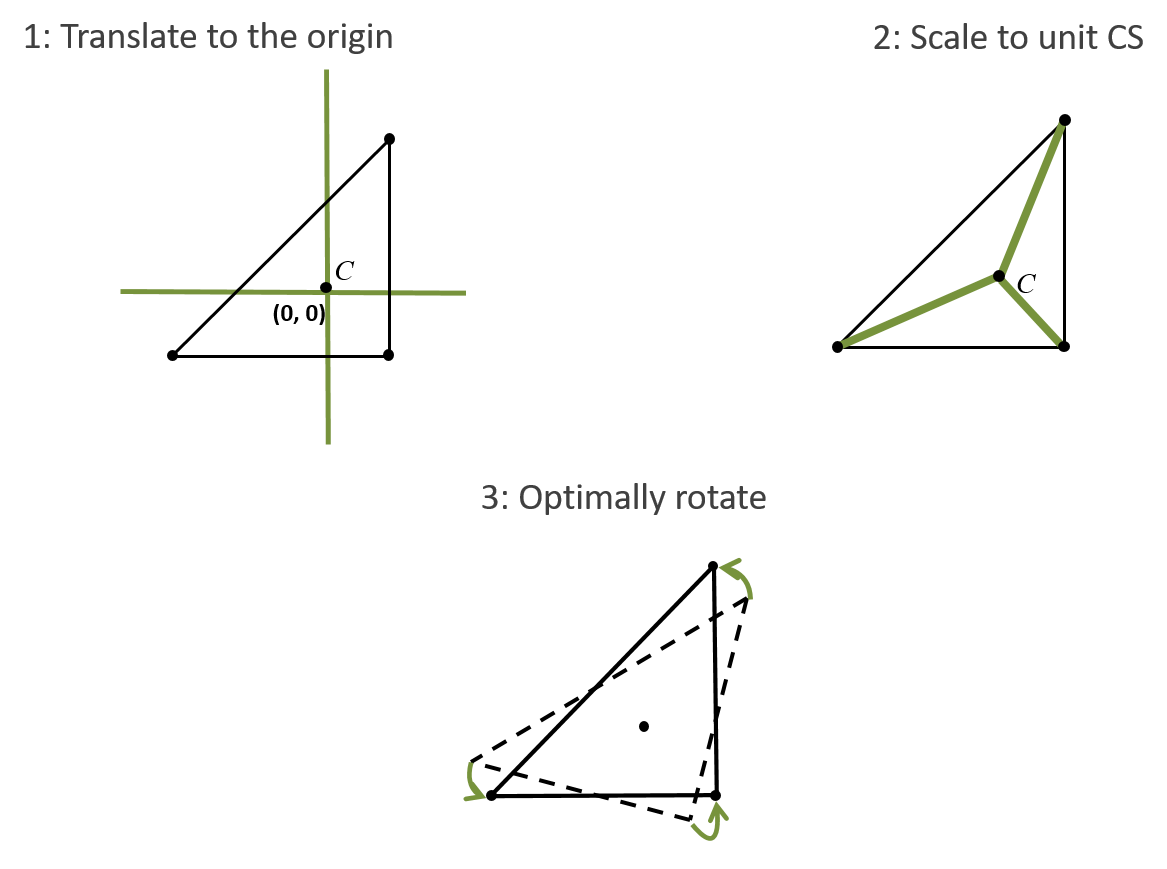
Análisis Multivariado del Morfoespacio
PCA y visualización morfológica
- Tras la superposición, las coordenadas 3D estandarizadas se analizan matemáticamente.
- PCA (Análisis de Componentes Principales): Agrupa la varianza para cuantificar y explorar los principales ejes de variación morfológica entre los especímenes.
- Visualización: Espacios morfológicos (morphospaces) donde cada punto es una forma.
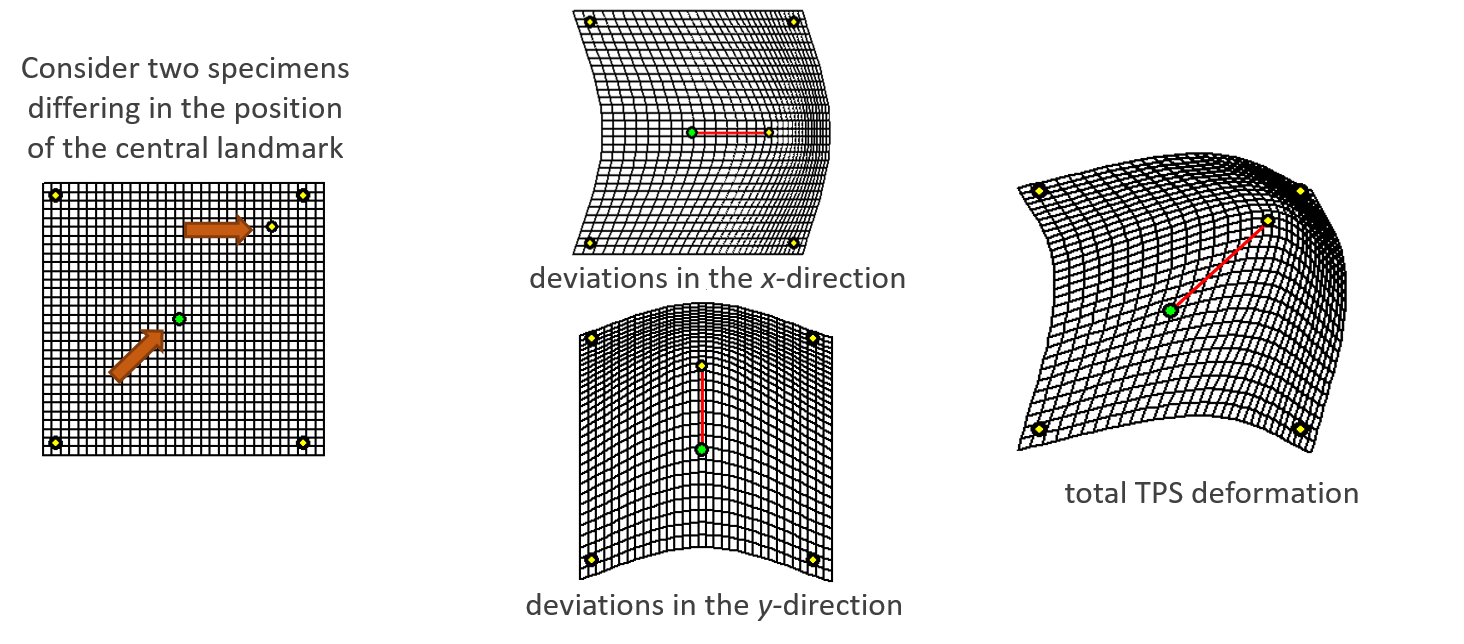
Thin-Plate Splines (TPS)
Interpolación espacial entre formas
- La morfometría geométrica se combina frecuentemente con simulaciones biomecánicas (como el FEA) utilizando algoritmos de interpolación espacial.
- Warping / Deformación: Permite doblar el espacio (y las mallas) de una configuración de landmarks de referencia hacia otra.
Aplicación Práctica del Warping
Deformación de mallas 3D
- Esta integración permite deformar (warp) la malla 3D de un cráneo o hueso conocido hacia morfologías hipotéticas.
- Útil para testear promedios genéricos, intermediarios evolutivos, o reconstruir especímenes fósiles (retrodeformación automatizada) para poner a prueba hipótesis de convergencia funcional.
Covariación de la Forma
Regresión multivariada y PLS
- El análisis estadístico frecuentemente se implementa usando regresiones multivariadas o PLS (Partial Least Squares).
- Asociación de variables: Permite usar la morfología multivariada como variable dependiente o independiente frente a otros datos, probando cómo se asocia estadísticamente con atributos de rendimiento (ej., fuerza de mordida o velocidad).
Alometría y Ecomorfología
Forma, tamaño y función
- Alometría Evolutiva: Un excelente ejemplo de covariación es modelar si el tamaño anatómico o la fuerza bruta dicta predeciblemente reglas sobre la geometría funcional de las palancas en el cráneo.
- Esto conecta la GMM directamente con ecofisiología y biomecánica evolutiva, probando por qué los cráneos tienen la forma que tienen según su función.
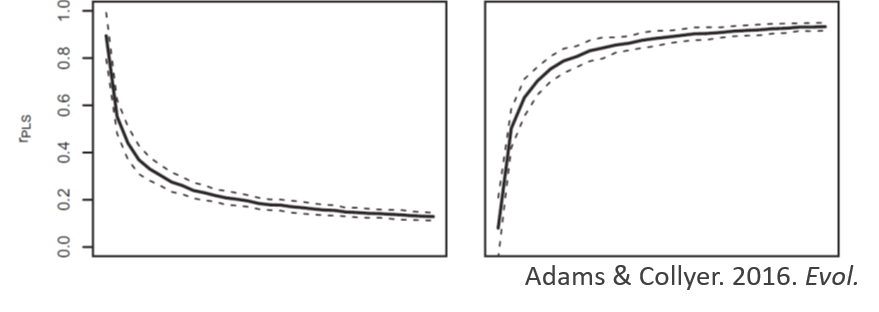
Paisaje Funcional
Topografía de rendimiento biomecánico
- Derivado del “Paisaje Adaptativo” evolutivo, un paisaje funcional grafica métricas de rendimiento biomecánico (ej. ventaja mecánica, energía de deformación) en un tercer eje frente a coordenadas morfológicas (Tseng, 2013).
- Modela un panorama de todas las morfologías teóricas posibles, originando una topografía de “picos” (óptimos biomecánicos) y “valles” (formas de bajo rendimiento).
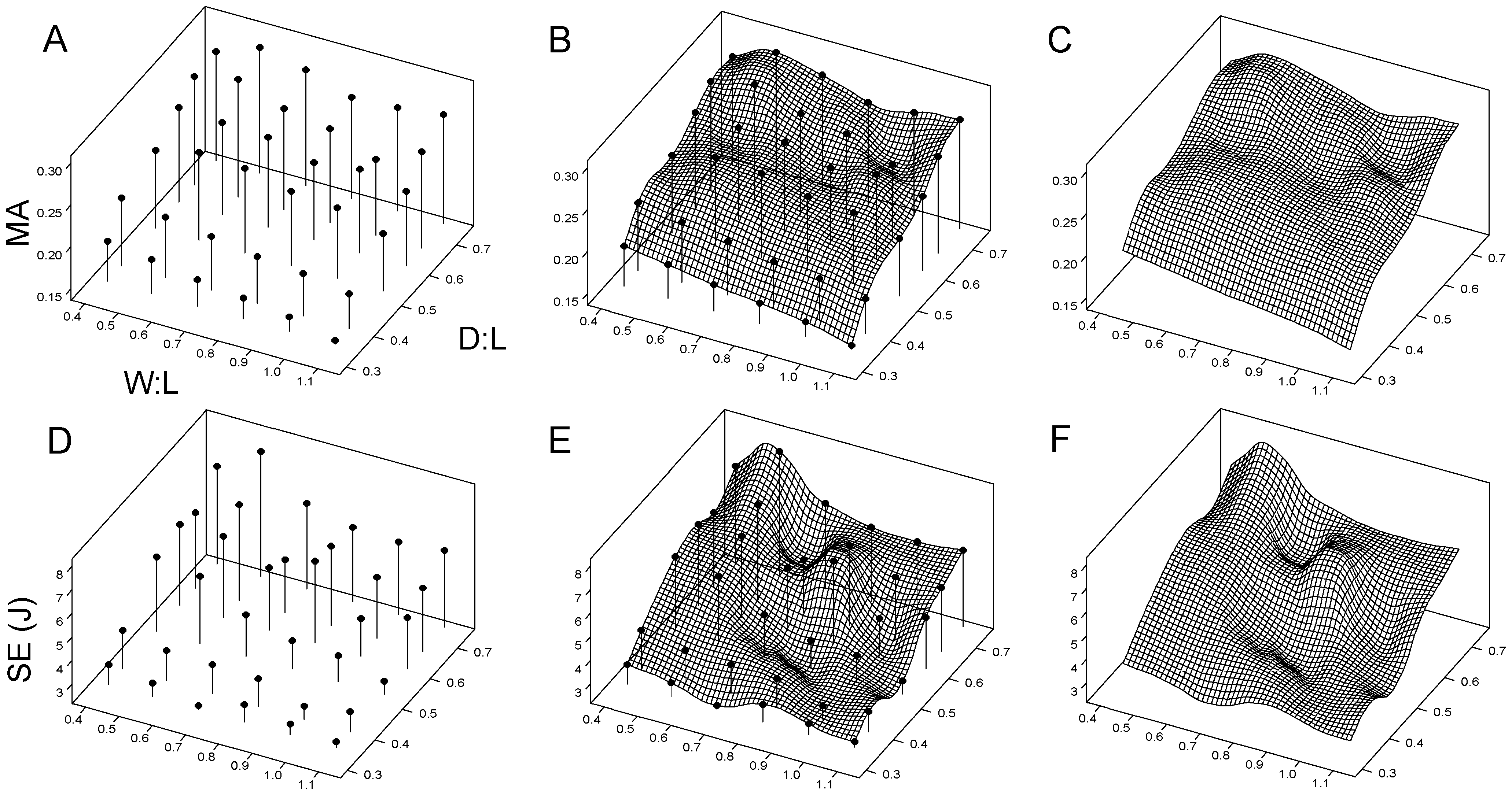
Convergencia Evolutiva
Trayectorias macroevolutivas
- Superponiendo trayectorias macroevolutivas reales de cráneos fósiles y actuales (ej. hienas, cánidos trituradores de hueso), se comprueba si la morfología evolucionó direccionalmente para escalar los picos óptimos de su nicho.
- Permite detectar casos donde la convergencia morfológica responde directamente a requerimientos mecánicos restrictivos para sobrevivir.
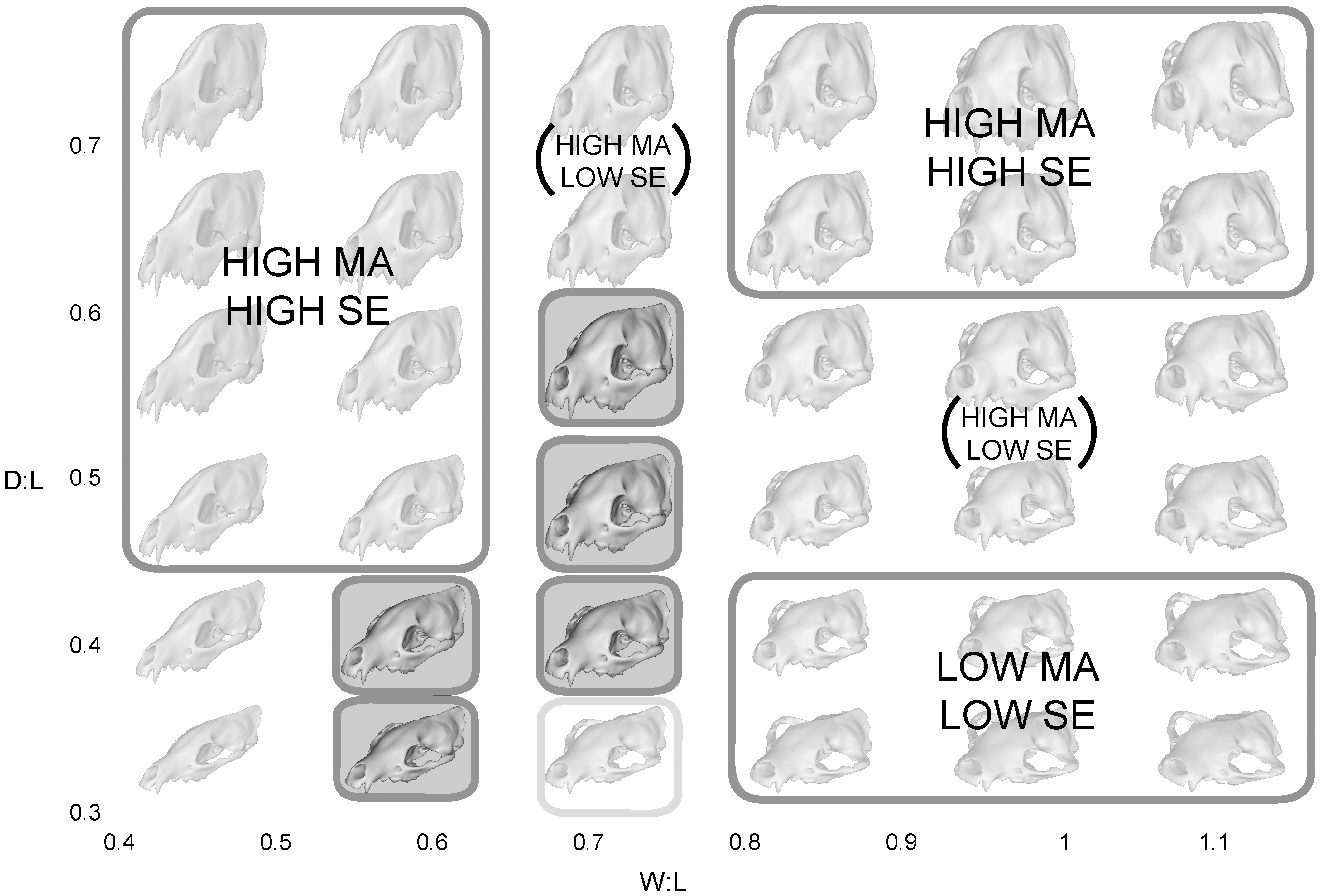
Práctica en R: GMM con Carnívora
La Base de Datos — Array de Landmarks 3D
set.seed(42)
# p landmarks × k coordenadas × n especímenes
craneos_3d <- array(
data = rnorm(20 * 3 * 30),
dim = c(20, 3, 30),
dimnames = list(
paste0("lm_", sprintf("%02d", 1:20)), # 20 landmarks
c("x", "y", "z"), # 3 coordenadas 3D
paste0("sp_", 1:30) # 30 especímenes
)
)
dim(craneos_3d) # p × k × nPaso 1 — Superposición de Procrustes (GPA)
gpagen()aplica la superposición generalizada de Procrustes en un paso.$coords— forma pura: sin escala, rotación ni traslación.$Csize— proxy del tamaño corporal; útil como covariable en análisis de alometría.
Paso 2 — PCA y Morfoespacio
# PCA sobre coordenadas de Procrustes
pca <- gm.prcomp(gpa$coords)
# Varianza explicada por cada componente
summary(pca)
# Morfoespacio (cada punto = un espécimen)
plot(pca,
main = "Morfoespacio — Carnívora",
pch = 19,
col = as.factor(familia))
legend("topright", legend = levels(familia),
pch = 19, col = 1:nlevels(familia))
Paso 3 — PLS: Forma vs. Fuerza de Mordida
# Vector de fuerza de mordida (un valor por espécimen, en N)
mordida_N <- c(...)
# PLS de dos bloques: ¿covaria la forma con la fuerza?
pls <- two.b.pls(
A1 = two.d.array(gpa$coords), # bloque 1: forma (matriz 2D)
A2 = log(mordida_N), # bloque 2: log-mordida
print.progress = FALSE
)
summary(pls) # r-PLS y p-valor permutacional
plot(pls,
main = "Covariación forma–mordida en Carnívora",
label = rownames(mordida_N))
Estimación de Máxima apertura mandibular y fuerza de mordida
Introducción a la Estimación de apertura mandibular
Modelando la función mandibular
- El rendimiento de la mordida, la cinemática de las mandíbulas y la tensión mecánica en animales extintos se analizan mediante simulaciones computacionales como el Análisis de Dinámica Multicuerpo (MDA) o FEA.
- Reconstrucción previa: Para estas estimaciones, es indispensable reconstruir la musculatura craneal (ej. los músculos aductores).
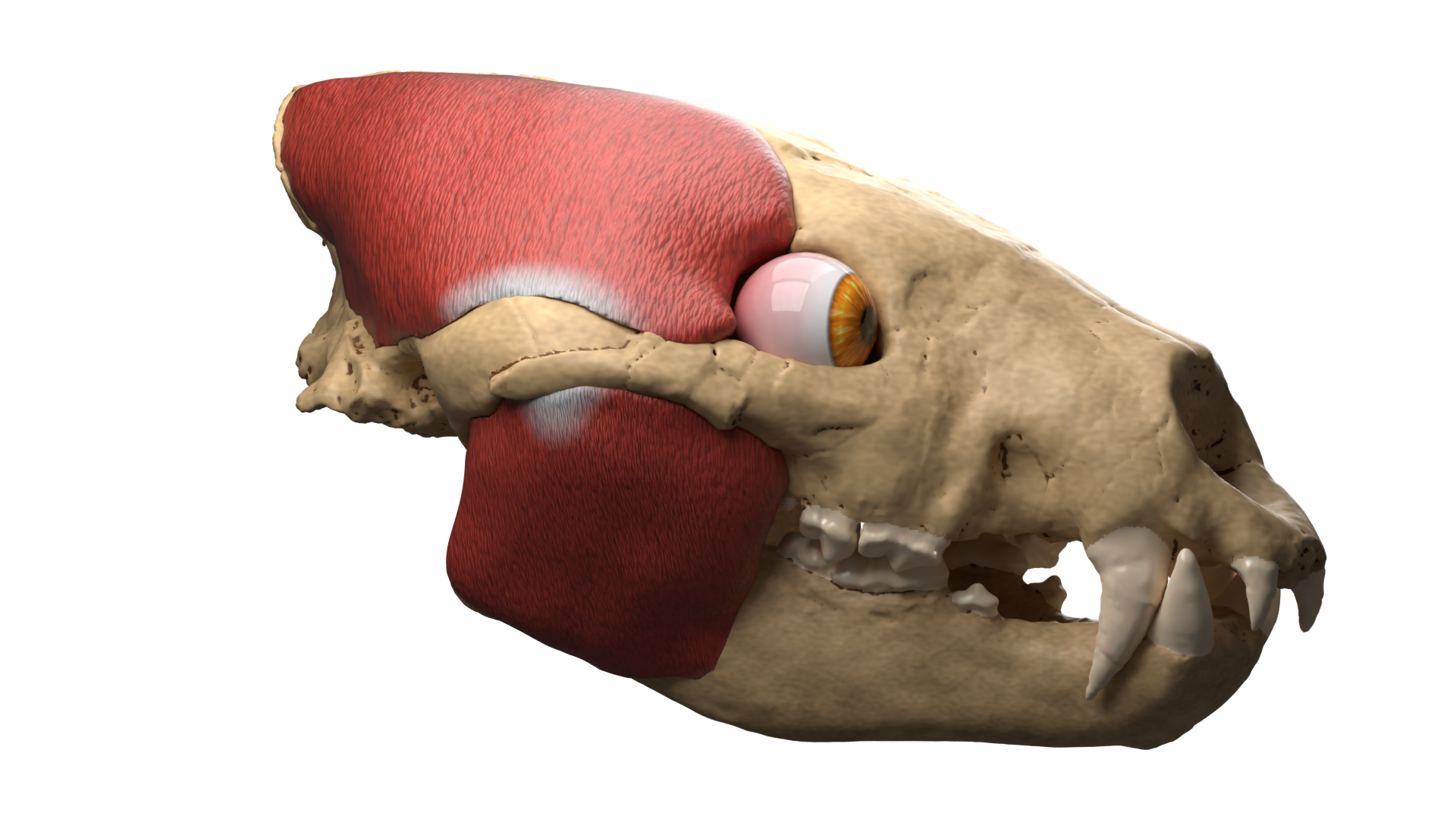
Cálculo del PCSA
Área de Sección Transversal Fisiológica
- La fuerza máxima (contracción isométrica) que puede generar un músculo fisiológico se calcula a partir de su Área de Sección Transversal Fisiológica (PCSA).
- Fórmula: PCSA se obtiene estimando el volumen tridimensional del músculo y dividiéndolo por la longitud de sus fibras multiplicada por el coseno de su ángulo de penación.
- Los cálculos pueden ser realizados mediante software especializado como MyoGeneratorRemix.
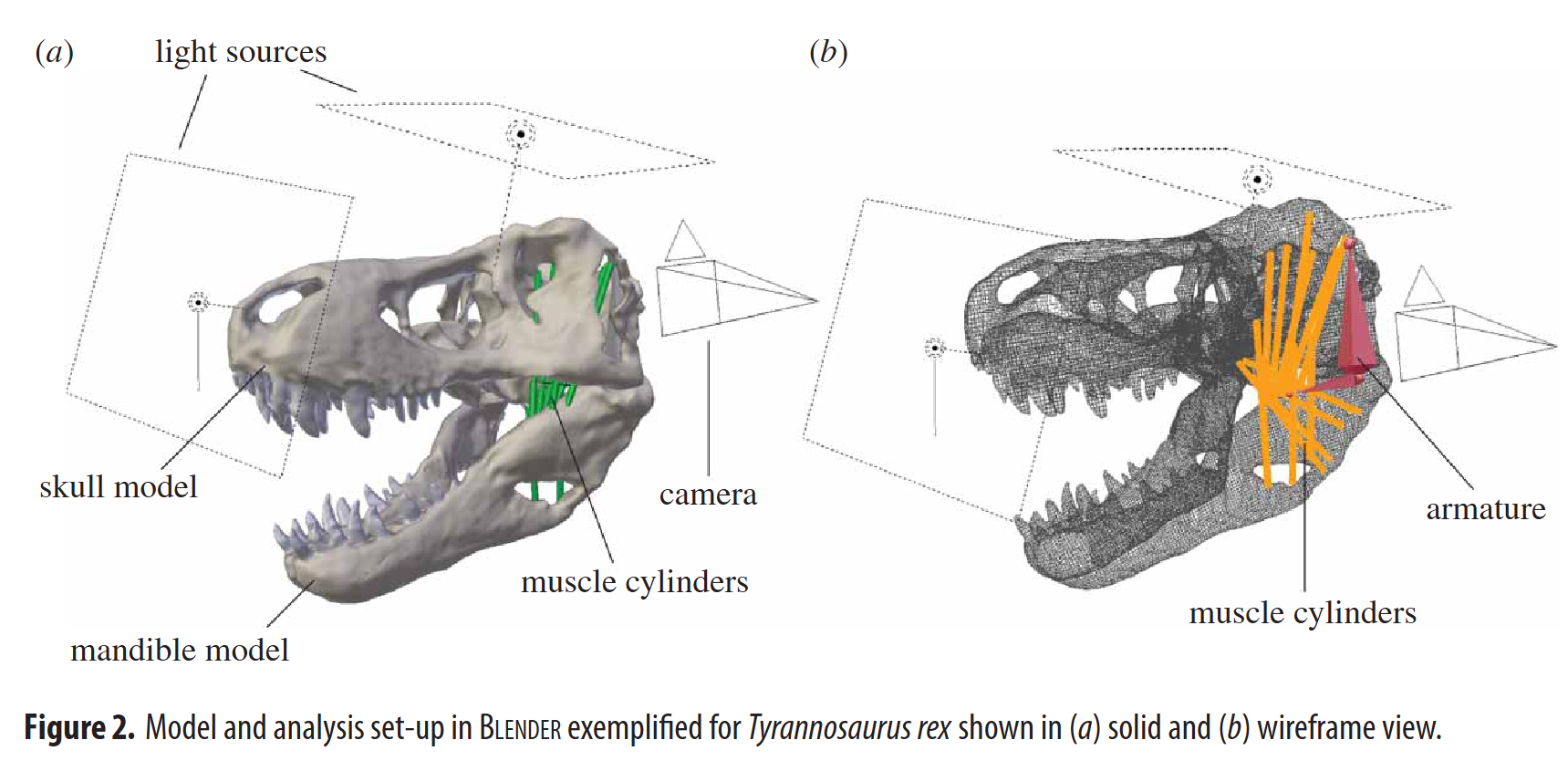
Metodología de Lautenschlager (Gape)
Estimación de Apertura Mandibular
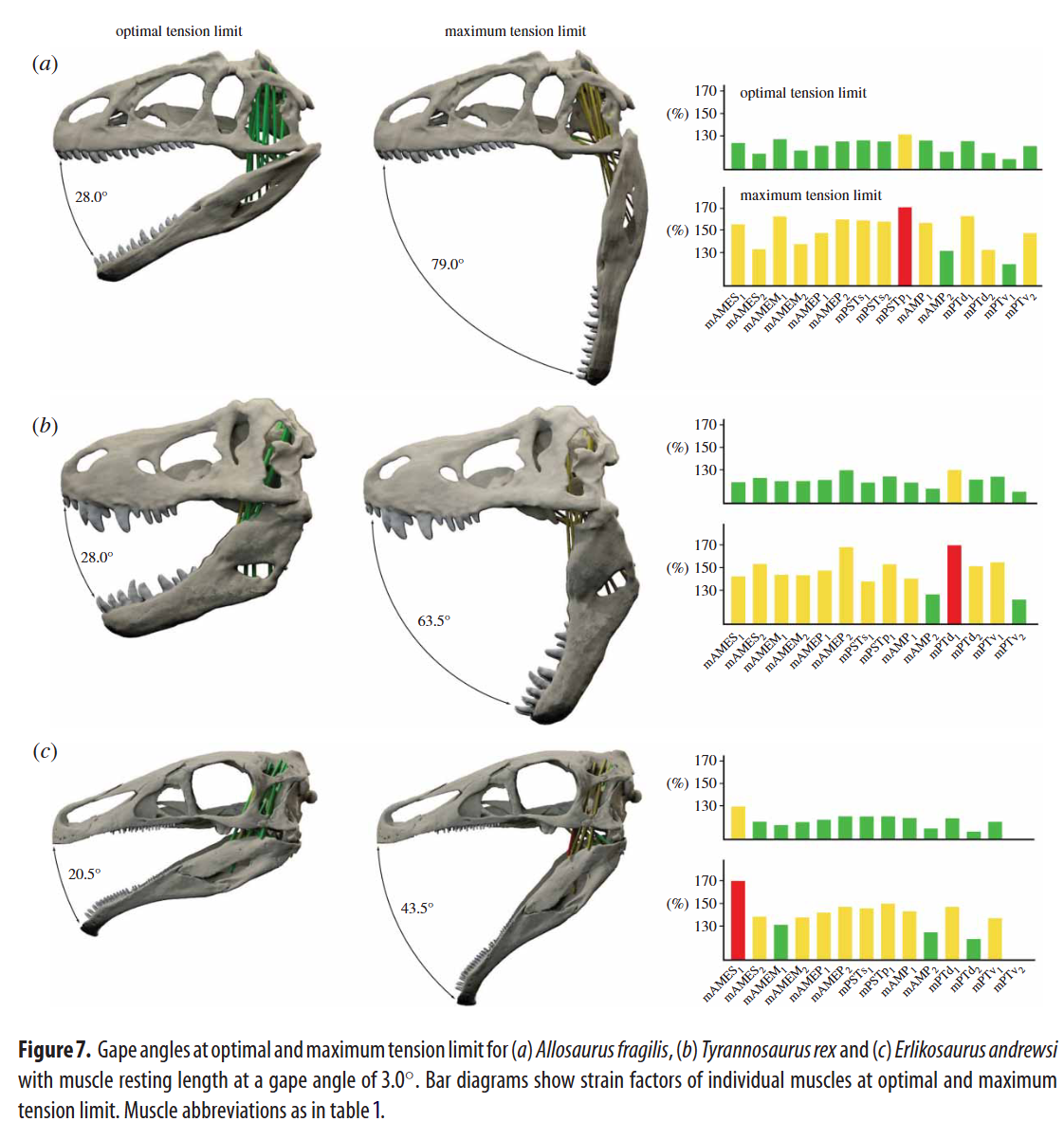
- La metodología de Stephan Lautenschlager se centra en calcular la apertura mandibular máxima (gape) a través de los límites de deformación muscular.
- Modelado de cilindros: Utilizando modelos 3D en Blender, los músculos aductores se modelan como primitivas (cilindros) anclados entre orígenes e inserciones.
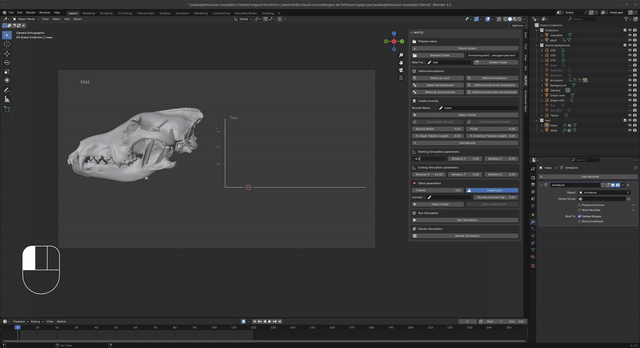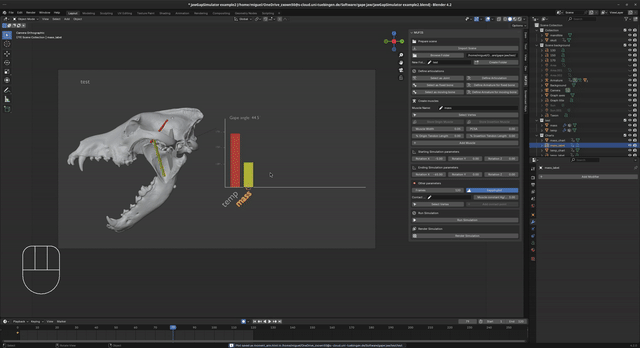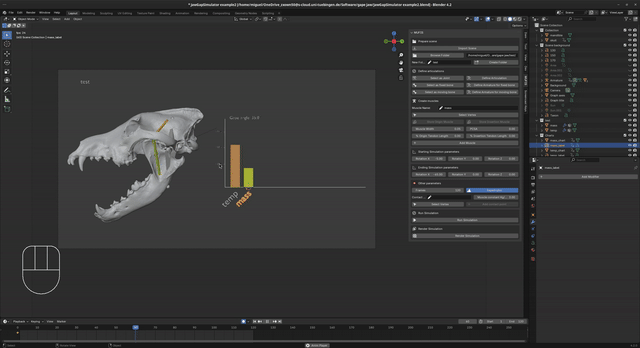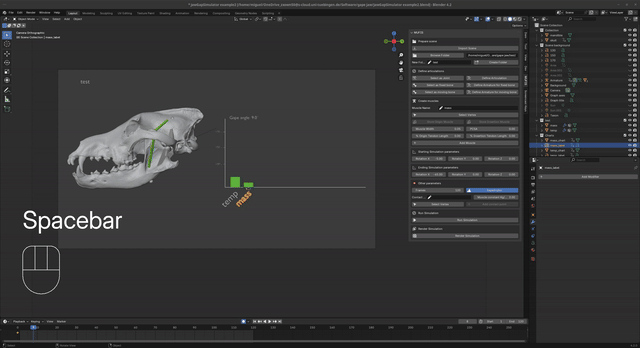
- Midiendo el estiramiento (strain) relativo conforme la mandíbula se abre, determina el límite de tensión óptimo y máximo fisiológico antes del desgarro (ej. 130%-170%).
Implementación MUFIS en Blender
Integración Dual Biomecánica
- Inicialmente los flujos 3D eran puramente visuales o requerían scripting manual. De ahí surge MUFIS (Muscle Fiber Simulator).
- Unifica dos métodos fundamentales:
- El método de Lautenschlager (2015) para evaluar y simular el factor de estiramiento y apertura mandibular máxima en la cinemática.
- El método de Hartstone-Rose et al. (2012) para estimar la fuerza de mordida real basada en el área seccional (PCSA) y los brazos de momento funcional.
- Calcula paramétricamente la fuerza isotrópica generada por cada cilindro muscular activo.
Bibliografía

E. Miguel Díaz de León Muñoz · Museo Virtual Nacional